PCR trong Pháp y
Phản ứng chuỗi polymerase (PCR) đã đóng một vai trò nền tảng trong sự hiểu biết của chúng ta về thế giới và có ứng dụng rộng rãi trong nhiều lĩnh vực khác nhau. Việc đưa PCR vào khoa học pháp y đã đánh dấu sự khởi đầu của một kỷ nguyên mới trong phân tích DNA. Kỷ nguyên này đã đẩy PCR đến giới hạn của nó và cho phép tạo ra dữ liệu di truyền từ DNA trong dấu vết. Các mẫu dấu vết chứa lượng rất nhỏ DNA bị phân hủy, đi kèm với các hợp chất và ion ức chế. Mặc dù đã có những phát triển đáng kể trong quy trình PCR kể từ khi nó lần đầu được giới thiệu, những thách thức trong việc phân tích các mẫu bị ức chế và phân hủy vẫn còn tồn tại.
Phản ứng chuỗi Polymerase & khoa học Pháp y
Nguyên lý chung của PCR
Phản ứng chuỗi polymerase (PCR) là một kỹ thuật nền tảng khuếch đại các vùng cụ thể của DNA thông qua một phản ứng được xúc tác bởi enzyme. Khuếch đại bằng PCR yêu cầu năm thành phần chính: các deoxynucleotide triphosphate (dNTPs), DNA polymerase chịu nhiệt, DNA khuôn, các mồi (primers) và một dung dịch đệm chứa kali và magiê. Tính đặc hiệu cao của PCR phần lớn là nhờ các mồi đặc hiệu theo trình tự có trong phản ứng và các điều kiện chu kỳ nghiêm ngặt. Chương trình PCR bao gồm ba bước cơ bản lặp đi lặp lại: biến tính (làm nóng để tách hai sợi của phân tử DNA), gắn mồi (để các mồi liên kết với trình tự đích bổ sung của chúng) và kéo dài (nhiệt độ được nâng lên cao hơn nhiệt độ gắn mồi một chút, tối ưu cho DNA polymerase tổng hợp phân tử DNA sợi kép mới). Ba bước này được lặp lại theo chu kỳ cho đến khi tạo ra đủ lượng DNA đích để có thể phát hiện được.
Các yếu tố thúc đẩy sự cải tiến của PCR trong khoa học Pháp y
Sự phát triển nhanh chóng của PCR và phân tích DNA trong những năm gần đây phần lớn có thể là do nhu cầu về độ nhạy cao, độ đặc hiệu và khả năng tái lặp trong các kỹ thuật pháp y. Lượng DNA tối ưu được nhà sản xuất khuyến nghị để tạo ra hồ sơ STR có giá trị chứng cứ đã giảm đáng kể, từ 2 ng năm 1995 xuống còn khoảng 0.4 ng trong các bộ kit STR hiện nay. Tuy nhiên, các mẫu pháp y thường được gửi để làm PCR với lượng DNA thấp hơn nhiều so với mức tối ưu, đẩy PCR đến giới hạn của nó. Quan trọng là khi độ nhạy của các kỹ thuật này tăng lên, số lượng mẫu DNA vết tích được gửi đến các phòng thí nghiệm để phân tích cũng tăng lên đáng kể. Mặc dù có những cải tiến về độ nhạy của máy móc và xét nghiệm PCR trong những năm gần đây, tỷ lệ thành công khi tạo hồ sơ DNA từ các mẫu vết tích này vẫn còn thấp.
Quy trình PCR hiện tại trong Pháp y
Quy trình PCR cho phân tích DNA, còn được gọi là PCR STR, sử dụng một dạng hóa học đặc biệt trong đó các chất phát huỳnh quang gắn vào mồi được kết hợp vào các đoạn khuếch đại (amplicon) khi phản ứng tiến triển. Sau khi PCR STR hoàn tất, sản phẩm khuếch đại được phát hiện trong quá trình điện di mao quản bằng cách sử dụng các thẻ huỳnh quang đã được kết hợp.
Tuy nhiên, trong các phòng thí nghiệm pháp y được công nhận, DNA có trong mẫu phải được định lượng trước khi tiến hành PCR STR để phân tích DNA. PCR định lượng (qPCR) cơ bản khác với PCR STR. Các bộ kit qPCR thương mại chẳng hạn như Investigator Quantiplex Pro sử dụng đầu dò TaqMan. Các đầu dò này được gắn hai thuốc nhuộm huỳnh quang: một thuốc nhuộm báo cáo ở đầu 5′ và một thuốc nhuộm dập tắt (quencher) ở đầu 3′. Khi đầu dò còn nguyên vẹn (trước khi trùng hợp), hai thuốc nhuộm ở gần nhau do kích thước nhỏ của đầu dò. Sự hiện diện của thuốc nhuộm dập tắt quá gần với thuốc nhuộm báo cáo có nghĩa là huỳnh quang của thuốc nhuộm báo cáo bị ức chế do sự chuyển năng lượng xảy ra giữa chúng. Sự chuyển giao năng lượng này dựa trên nguyên lý chuyển giao năng lượng cộng hưởng huỳnh quang (FRET). Khi một qPCR được thực hiện, các đầu dò liên kết với các trình tự đích trong giai đoạn gắn mồi và huỳnh quang của thuốc nhuộm báo cáo vẫn bị ức chế. Tuy nhiên, trong giai đoạn kéo dài, hoạt tính exonuclease 5′ của DNA polymerase làm giải phóng các đầu dò TaqMan đã liên kết và thuốc nhuộm báo cáo gắn ở đầu 5′ được tách ra khỏi thuốc nhuộm dập tắt ở đầu 3′. Sự phân tách này có nghĩa là sự ức chế huỳnh quang khi hai chất phát huỳnh quang ở gần nhau không còn xảy ra nữa và phân tử báo cáo bây giờ có thể phát huỳnh quang. Lượng huỳnh quang được phát hiện tương quan trực tiếp với lượng DNA có trong phản ứng, vì lượng DNA càng nhiều thì càng nhiều phân tử thuốc nhuộm báo cáo bị cắt ra và lượng huỳnh quang được phát hiện càng lớn. Thông thường, khi chương trình qPCR tiến triển và DNA tăng theo cấp số nhân, một đường cong khuếch đại được tạo ra bằng cách sử dụng các dữ liệu huỳnh quang này, sau đó (vào cuối chương trình qPCR) được sử dụng để tính toán nồng độ DNA. Nếu một mẫu được phát hiện có chứa đủ lượng DNA, để có thể thu được thông tin di truyền hữu ích từ nó, thì mẫu đó có thể tiến hành PCR STR và có thể tạo ra hồ sơ DNA.
Sự cải tiến điều kiện chu kỳ PCR trong Pháp y
Phân tích STR
Việc đưa thêm các locus STR vào hỗn hợp đa hợp (multiplex) PCR đồng nghĩa với việc số lượng mồi cần thiết để khuếch đại các vùng đa hình cao này tăng lên và cùng với đó là tính nghiêm ngặt của giai đoạn gắn mồi. Với việc bổ sung các locus STR mới, nhiều mồi hơn được thêm vào PCR để đảm bảo rằng các locus mới sẽ được khuếch đại cho tất cả các quần thể người trên toàn thế giới. Các mồi này cũng cần có khả năng liên kết với trình tự bổ sung của chúng và tránh ghép sai; do đó, để đảm bảo khuếch đại chính xác, các điều kiện chu kỳ PCR được sử dụng ngày nay rất nghiêm ngặt. Do tính nghiêm ngặt này và để cải thiện hơn nữa chất lượng hồ sơ DNA thu được từ các mẫu thách thức (ví dụ: vật liệu bị ức chế và vết tích), những thay đổi đã được thực hiện đối với các yếu tố khác của quá trình khuếch đại (ví dụ: dung dịch đệm, enzyme, thiết bị).
Mặc dù đã có những thay đổi nhỏ đối với các điều kiện chu kỳ được khuyến nghị giữa các bộ kit, các điều kiện phần lớn không đổi tương tự nhau thường được sử dụng trong các bộ kit STR đa hợp thương mại đã được kiểm chứng. Trong nỗ lực tăng tỷ lệ thành công của phân tích DNA đối với các mẫu DNA khuôn thấp (low-template), số chu kỳ PCR có thể được tăng lên từ một đến năm chu kỳ. Việc bổ sung thêm chu kỳ khuếch đại hữu ích trong việc thu được nhiều hồ sơ DNA hơn từ các mẫu khuôn thấp, nhưng đó không phải là một sự thay đổi đối với các điều kiện chu kỳ PCR, mà chỉ là một lần lặp lại thêm của các điều kiện khuếch đại đồng nhất giống nhau.
DNA Ty thể – mtDNA
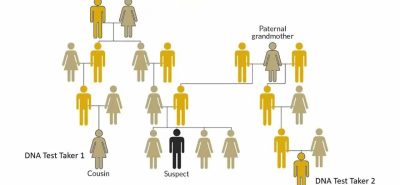
Song song với sự ra đời của khuếch đại STR cho phân tích DNA, khuếch đại DNA ty thể (mtDNA) cho phân tích pháp y cũng được thực hiện vào đầu những năm 1990. Việc khuếch đại nhắm mục tiêu ba vùng siêu biến đổi tương đối nhỏ trong bộ gene ty thể người, HV1, HV2 và HV3, cung cấp một phương tiện nhận dạng thay thế khi các nguồn DNA nhân truyền thống (ví dụ: dịch cơ thể và mô) không còn khả dụng. Sức mạnh của mtDNA trong việc cung cấp thông tin khi các phương pháp tiêu chuẩn thất do có hàng nghìn ty thể trong mỗi tế bào, mỗi ty thể có từ 2 đến 10 bản sao mtDNA. Tuy nhiên, không giống như DNA nhân được nhắm mục tiêu cho phân tích STR, mtDNA chỉ được di truyền theo dòng mẹ. Do đó, phân tích mtDNA có khả năng xác định các cá nhân có quan hệ theo dòng mẹ (ví dụ: anh chị em), cũng như phân biệt giữa các cá nhân từ các dòng mẹ khác nhau. Giá trị của các dấu chuẩn này rõ ràng nhất khi xác định người mất tích, hài cốt người không xác định và nạn nhân thảm họa.
Trong khi một trong những yếu tố chính ảnh hưởng đến điều kiện chu kỳ PCR cho phân tích STR là số lượng mục tiêu cần thiết để tạo ra các hồ sơ có khả năng phân biệt cao, thì các điều kiện chu kỳ được sử dụng để khuếch đại mtDNA không phải đối mặt với những hạn chế tương tự vì ít vùng được nhắm mục tiêu hơn. Điều này là do trước khi sử dụng các nền tảng giải trình tự song song khối lượng lớn (MPS), tất cả các phản ứng khuếch đại mtDNA đều được thực hiện với một cặp mồi. Số lượng mồi ít hơn cần thiết cho phân tích mtDNA có nghĩa là có sự linh hoạt trong giai đoạn gắn mồi mà phân tích STR hoặc SNP không có. Hầu hết các thách thức của phân tích mtDNA nằm ngoài quy trình PCR. Sự biến đổi vốn có trong bộ gene ty thể của một cá nhân, được gọi là hiện tượng dị bội (heteroplasmy) và sự dễ bị nhiễm bẩn tăng lên trong quá trình chiết xuất mtDNA tạo ra những thách thức đáng kể cho việc giải thích mtDNA. Không giống như PCR STR, việc duy trì các quy trình khuếch đại mtDNA có thể là kết quả của việc các phòng thí nghiệm pháp y tuân thủ các hướng dẫn do Hiệp hội Di truyền học Pháp y Quốc tế đưa ra cho phân tích mtDNA như một phương tiện kiểm soát chất lượng. Nhu cầu kiểm soát chất lượng trong phân tích mtDNA được tăng cường do thiếu các bộ kit PCR thương mại. Tất cả các bộ kit PCR STR thương mại đều đi kèm với các điều kiện chu kỳ được khuyến nghị đã được nhà sản xuất kiểm chứng kỹ lưỡng. Điều này có nghĩa là các phòng thí nghiệm chỉ cần xác minh bộ kit trước khi triển khai trong công tác vụ án. Việc thiếu các bộ kit mtDNA thương mại có nghĩa là không có sự kiểm chứng trước tương tự đằng sau các điều kiện PCR được sử dụng, cho phép nhiều biến thể hơn trong các điều kiện chu kỳ có thể được sử dụng để khuếch đại mtDNA giữa các phòng thí nghiệm.
Do bản chất khuôn thấp và phân hủy của các mẫu thường được gửi để phân tích mtDNA (ví dụ: xương, răng và tóc), một số thay đổi đã được thực hiện đối với số chu kỳ PCR được sử dụng để khuếch đại các mục tiêu mtDNA. Số chu kỳ bổ sung dao động từ 2 đến 12 chu kỳ cao hơn so với PCR STR trong nỗ lực tối đa hóa lượng dữ liệu ty thể thu được từ các mẫu thách thức này. Tuy nhiên, như đã đề cập trước đó, việc bổ sung thêm các chu kỳ PCR không thực sự là một sự thay đổi đối với các điều kiện chu kỳ, mà chỉ là sự lặp lại của các điều kiện đồng nhất giống nhau. Các bước biến tính, gắn mồi và kéo dài ngắn hơn được sử dụng trong các chương trình PCR mtDNA hiện tại có thể là do các thiết bị và thuốc thử PCR được cải thiện; tuy nhiên, nó cũng cung cấp một số bằng chứng để hỗ trợ cho đề xuất rằng thời gian của các giai đoạn có thể được rút ngắn mà không ảnh hưởng đến khuếch đại đích. Những thách thức mà hiện tượng dị bội và nhiễm bẩn tiếp tục đặt ra cho phân tích mtDNA không phụ thuộc vào PCR và do đó không thể khắc phục bằng cách thay đổi quy trình PCR. Tuy nhiên, tiềm năng tối ưu hóa các phương pháp khuếch đại mtDNA bằng cách sử dụng các chương trình PCR không đồng nhất thay đổi khi điều kiện trong ống PCR thay đổi vẫn còn tồn tại.
Phân tích Đa hình Đơn Nucleotide – SNPs
Mặc dù khuếch đại các đa hình đơn nucleotide (SNPs) cho phân tích pháp y đã được sử dụng trong công tác vụ án trước khi phân tích STR, nhưng các vấn đề liên quan đến việc tạo các phản ứng đa hợp SNP và khả năng phân biệt thấp hơn đáng kể do hồ sơ SNP mang lại đã khiến phân tích STR trở thành kỹ thuật chính để nhận dạng người. Tuy nhiên, phân tích SNP tiếp tục được phát triển để đáp ứng nhu cầu về các kỹ thuật nhanh hơn và đáng tin cậy hơn để khuếch đại các mẫu bị phân hủy cao và vết tích. Ngoài ra, có nhiều SNP trên cả DNA nhân và mtDNA, cho phép phân tích bằng công nghệ này nhắm mục tiêu cả hai loại DNA.
Trong những năm gần đây, phân tích SNP đã nổi lên như một nhân tố chính trong lĩnh vực di truyền học pháp y do phạm vi thông tin rộng mà nó có thể cung cấp từ các đoạn khuếch đại nhỏ. Điều này là vì các biến thể nucleotide đơn rất phong phú trong bộ gene người do quá trình đột biến. Khi số lượng SNP được xác định là có tính biến đổi cao trong bộ gene người tiếp tục tăng, khả năng phân biệt giữa các bộ gene khi áp dụng vào điều tra pháp y cũng tăng theo. Do sự phong phú của các SNP có liên quan đến pháp y, chúng được chia thành năm loại chính dựa trên loại thông tin mà chúng có thể cung cấp cho các nhà điều tra. Các loại này là SNP thông tin nhận dạng (iiSNPS), SNP thông tin dòng dõi (liSNPs), SNP thông tin tổ tiên (aiSNPs), SNP thông tin kiểu hình (piSNPs) và SNP dược di truyền (pharmacogenetic). Sự kết hợp của các SNP này có thể cung cấp cái nhìn sâu sắc về tổ tiên địa lý sinh học (BGA) và các đặc điểm hình thái bên ngoài (EVCs) của một cá nhân, ngoài khả năng nhận dạng người mà các xét nghiệm STR và mtDNA mang lại, điều này làm nổi bật giá trị của phân tích SNP đối với các cuộc điều tra pháp y.
Có những điểm tương đồng rõ ràng giữa các chương trình PCR mtDNA và STR đã đề cập trước đó và các điều kiện chu kỳ được sử dụng cho phân tích SNP. Tuy nhiên, điều này không có gì ngạc nhiên, vì phản ứng đa hợp SNP được phát triển nhằm cố gắng khắc phục một số thách thức liên quan đến việc phân tích các mẫu mtDNA và STR bị phân hủy và khuôn thấp. Sự khác biệt trong các điều kiện chu kỳ PCR giữa các xét nghiệm SNP phần lớn có thể là do sự kết hợp khác nhau của các mục tiêu SNP được sử dụng và do đó sự kết hợp khác nhau của các mồi yêu cầu các điều kiện gắn mồi khác nhau để đảm bảo tất cả các mục tiêu được khuếch đại đồng đều và hiệu quả. Trong khi các xét nghiệm ban đầu nhắm mục tiêu 12 SNP riêng lẻ, các bảng SNP được phát triển gần đây hơn, chẳng hạn như những bảng được sử dụng cho các ứng dụng phả hệ di truyền điều tra pháp y (FIGG) hiện đại, nhắm mục tiêu tới 1 triệu SNP riêng lẻ trong một xét nghiệm duy nhất. Việc bổ sung một số lượng lớn các mục tiêu SNP mới cũng là lý do tại sao các điều kiện chu kỳ đã được bảo tồn cao, vì tất cả các mục tiêu cần được khuếch đại một cách cân bằng và do đó, có các điều kiện gắn mồi rất nghiêm ngặt. Việc tăng số chu kỳ PCR một lần nữa có thể là do sự thúc đẩy để thu được lượng dữ liệu di truyền ngày càng nhiều từ phân tích SNP. Tuy nhiên, như đã lưu ý trước đó, sự khác biệt về số chu kỳ chỉ thể hiện thêm các lần lặp lại của cùng một điều kiện PCR đồng nhất và không phải là sự thay đổi thực tế đối với các điều kiện chu kỳ. Cũng như phân tích STR, những thay đổi đã được thực hiện đối với các yếu tố khác của quy trình PCR (ví dụ: dung dịch đệm thương mại, enzyme, thiết bị) để giúp cải thiện hơn nữa hiệu quả khuếch đại, và do đó là chất lượng tổng thể của dữ liệu SNP thu được.
Mặc dù thành công của phân tích SNP trong những năm gần đây, kỹ thuật này đã bắt đầu chuyển hướng khỏi các phương pháp khuếch đại đích truyền thống, chẳng hạn như PCR, sang các công nghệ mới giải trình tự các phân tử DNA trực tiếp mà không cần bất kỳ PCR nào. Công nghệ như Sequencing by synthesis được sử dụng trong máy Miseq FGx của QIAGEN cung cấp các phương pháp thông lượng cao hơn cho phân tích SNP. Do đó, trong khi tiềm năng tồn tại để các chương trình PCR SNP được tối ưu hóa hơn nữa bằng cách sử dụng các điều kiện chu kỳ thay đổi dần dần để tính đến những thay đổi trong hoạt tính enzyme trong suốt quá trình chạy, thì sự chuyển hướng từ các nền tảng giải trình tự Sanger truyền thống yêu cầu PCR sang các công nghệ thế hệ tiếp theo không yêu cầu PCR cho thấy rằng có lẽ sự phát triển của phân tích SNP nằm ngoài quy trình PCR.
Mặc dù các quy trình PCR được sử dụng cho phân tích STR, xét nghiệm mtDNA và phân tích SNP đều đã phát triển đáng kể kể từ khi lần đầu tiên được giới thiệu vào khoa học pháp y, nhưng sự tiến hóa một nhanh đã chậm lại đáng kể trong những năm gần đây. Mặc dù điều này không nhất thiết là một vấn đề đối với phân tích mtDNA và SNP, nhưng các vấn đề đặc trưng của việc giải thích các mẫu bị phân hủy và ức chế cho phân tích STR vẫn đặt ra những hạn chế đáng kể cho phân tích DNA. Tuy nhiên, các ngành khác, chẳng hạn như khoa học y tế, đã tiếp tục chứng kiến sự tiến hóa nhanh chóng của quy trình PCR, và kết quả là, các biến thể PCR rất thành công đã được phát triển và tích hợp vào quy trình làm việc của họ.
Bài viết được tham khảo từ bài báo PCR in Forensic Science: A Critical Review
Để tìm hiểu chi tiết thêm về ứng dụng và tính năng của các sản phẩm phục vụ cho quá trình xác định danh tính, huyết thống, vui lòng liên hệ chúng tôi để được hỗ trợ tư vấn trực tiếp.